Fusion分析
前言
IMPORTANT
Fusion模块专注于单细胞转录组融合基因检测分析,通过结合STAR-Fusion算法和单细胞转录组数据,实现细胞水平的融合基因鉴定、可视化和功能分析。流程支持human和mouse物种,能够从原始fastq文件或预处理数据中识别融合事件,并在单细胞分辨率上进行展示。
基因融合作为重要的分子事件,在肿瘤发生、细胞分化和疾病进展中扮演着关键角色。SeekSoulOnline云平台的Fusion模块提供了从原始数据处理到结果可视化的完整解决方案,能够准确识别融合基因、评估其在不同细胞群体中的分布,并提供详细的生物学注释信息。
Fusion分析理论基础
核心原理
- 数据预处理:对输入的fastq文件进行质控和过滤,去除低质量reads和接头序列,确保后续分析的准确性。
- 融合基因检测:使用STAR-Fusion算法进行融合事件识别,该算法结合了STAR比对器的高灵敏度和专用的融合过滤流程,能够有效识别各种类型的基因融合。
- 融合验证与注释:对检测到的融合事件进行验证,评估其可靠性,并提供丰富的注释信息,包括断点位置、支持reads数、融合类型等。
- 单细胞整合分析:将融合基因检测结果与单细胞转录组数据整合,识别携带特定融合的细胞群体。
- 可视化与报告生成:生成UMAP/TSNE可视化图,直观展示融合基因在不同细胞群体中的分布,并生成包含详细分析结果的HTML报告。
技术特点
| 特点 | 说明 | 优势 |
|---|---|---|
| STAR-Fusion算法 | 基于STAR比对器,能够高效识别融合转录本 | 高灵敏度、低假阳性率 |
| 单细胞水平解析 | 将融合事件映射到特定细胞群体 | 提供细胞异质性视角 |
| 多物种支持 | 支持human和mouse基因组分析 | 适用范围广 |
| 丰富的注释信息 | 提供断点位置、融合类型、功能注释等 | 便于生物学解读 |
| 直观的可视化 | UMAP/TSNE散点图展示融合基因分布 | 便于结果解释和展示 |
关键统计指标
- JunctionReadCount:包含在融合连接位点处,一条read可以拆分匹配到两侧融合基因的reads数量。
- SpanningFragCount:包含融合连接的reads数量,该reads的R1端和R2端对应基因不同。
- FFPM:支持融合的reads的标准化结果,即每百万总reads数的融合量。
- LargeAnchorSupport:在假定断点两侧是否存在reads的较长碱基序列(≥25)匹配,缺少LargeAnchorSupport的融合基因通常为假阳性。
- PROT_FUSION_TYPE:蛋白质融合类型,如INFRAME(框内融合)等。
SeekSoulOnline云平台操作指南
分析前准备
CAUTION
- 输入数据应为成对的fastq文件(R1和R2),确保文件命名规范,便于系统正确识别样本信息。
- 确保选择正确的物种(human或mouse),这将影响参考基因组的选择和后续分析的准确性。
- 对于大规模数据,建议先进行数据质量评估,确保数据质量满足分析要求。
参数详解
| 界面参数 | 说明 | 备注 |
|---|---|---|
| 任务名称 | 英文开头,可含中文/数字/下划线 | 用于报告抬头与任务跟踪 |
| 样本信息 | 输入样本名称、R1和R2 fastq文件路径 | 支持多个样本并行分析 |
| 物种 | human / mouse | 决定使用的参考基因组 |
| 备注 | 自定义文本 | 记录分析背景信息 |

结果解读
结果目录速览
| 路径 | 内容 | 说明 |
|---|---|---|
output/results/fusion/ | 融合基因检测原始结果 | 包含STAR-Fusion输出文件 |
output/results/plots/ | 融合基因可视化图表 | UMAP/TSNE散点图 |
output/results/meta/ | 元数据信息 | 细胞注释和统计数据 |
report/ | HTML报告目录 | 包含完整分析结果的报告 |
融合基因表格解读
| 列名 | 说明 | 重要性 |
|---|---|---|
#FusionName | 融合基因名称 | 主键标识符 |
JunctionReadCount | 连接位点支持reads数 | 评估可信度 |
SpanningFragCount | 跨融合片段reads数 | 评估可信度 |
LeftGene/RightGene | 融合涉及的两个基因 | 功能分析基础 |
LeftBreakpoint/RightBreakpoint | 融合断点位置 | 结构分析关键 |
LargeAnchorSupport | 长锚点支持情况 | 过滤假阳性重要指标 |
FFPM | 融合reads标准化值 | 定量表达水平 |
PROT_FUSION_TYPE | 蛋白质融合类型 | 功能预测依据 |
关键图表示例
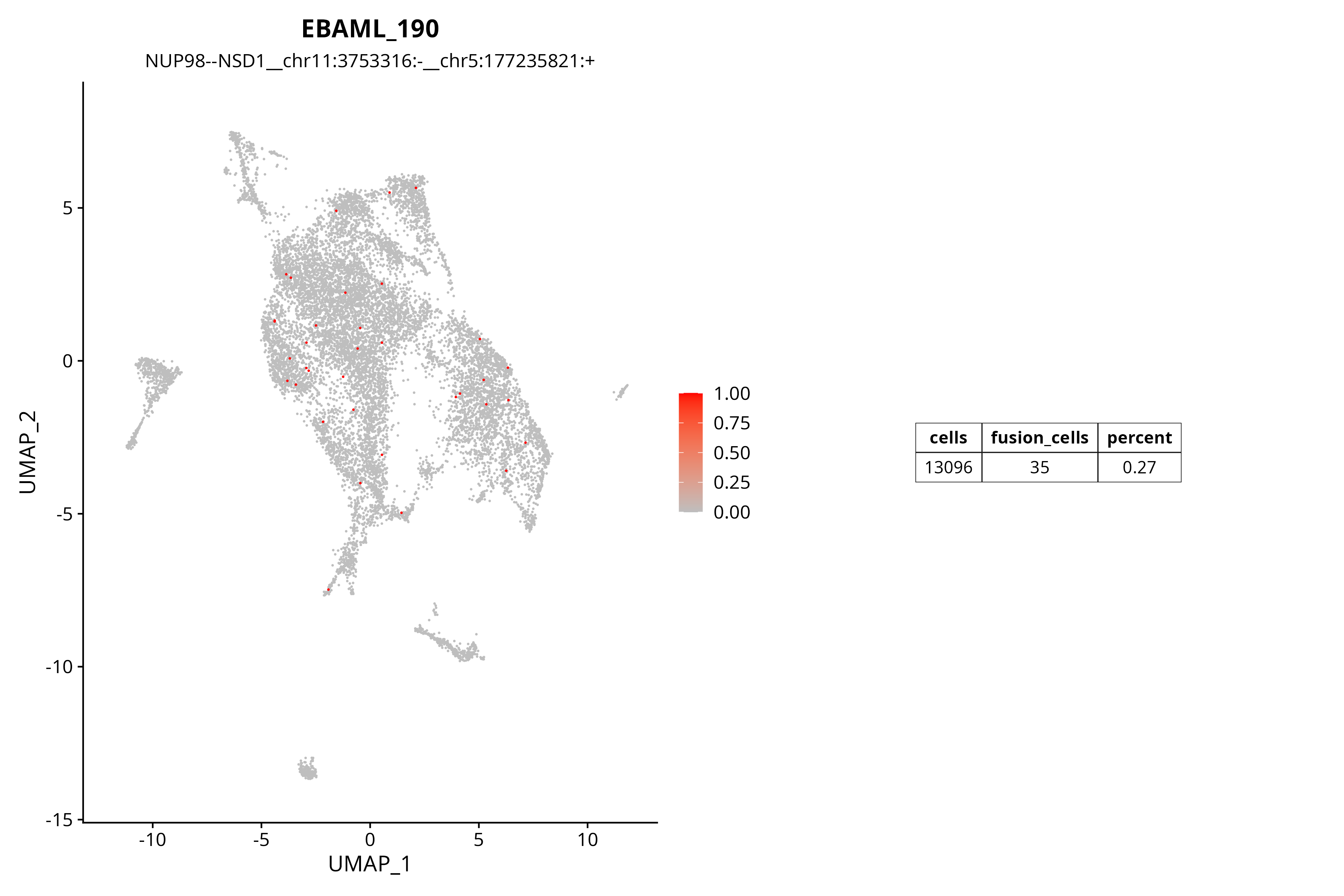
融合基因UMAP分布图
下图展示了NUP98--NSD1融合基因在单细胞群体中的分布情况。颜色深浅表示UMI计数,红色表示高表达该融合的细胞。
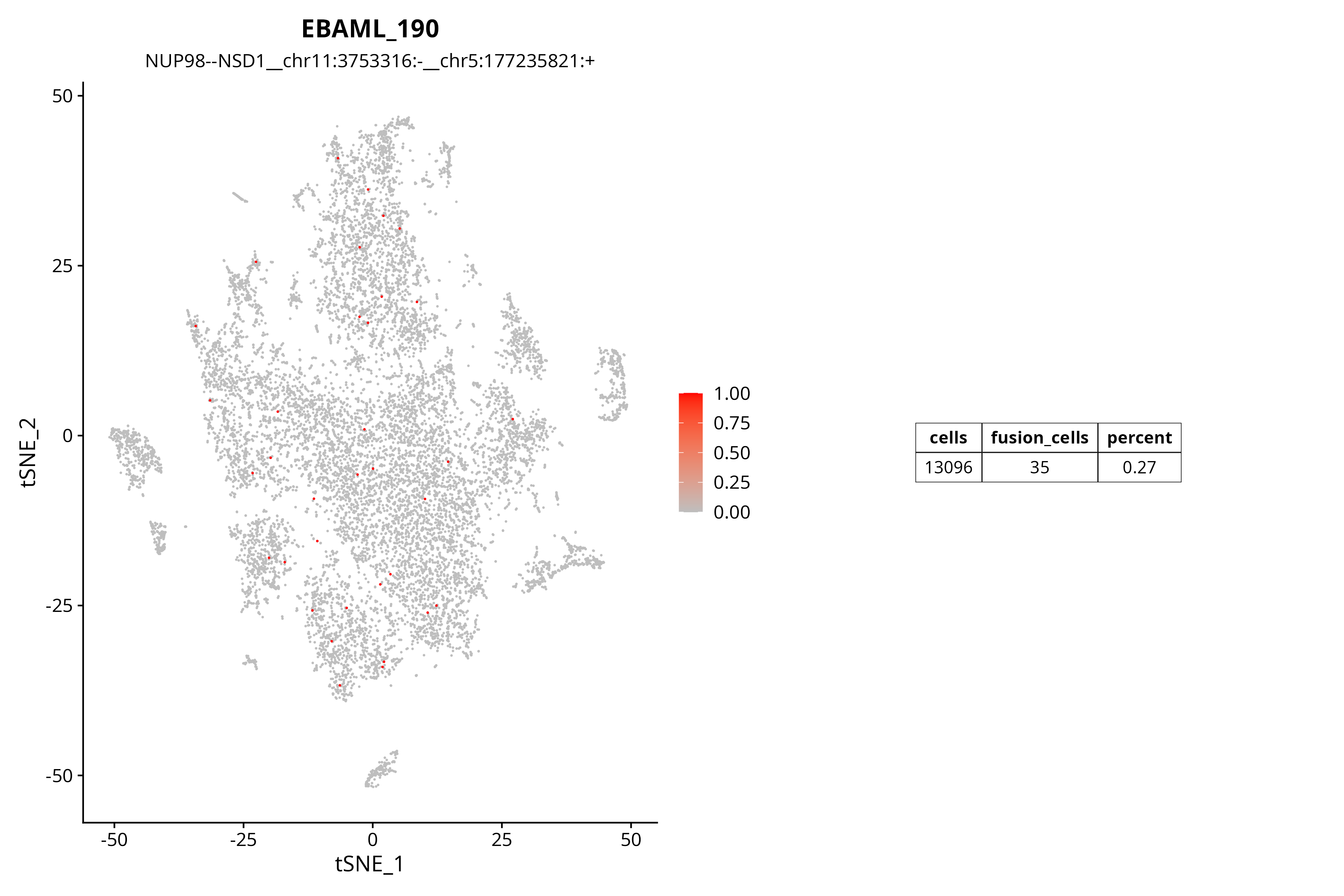
融合基因TSNE分布图
TSNE图提供了另一种可视化视角,有助于识别融合基因在不同细胞亚群中的分布模式。
生物学意义解读
- 功能分类:根据融合基因的注释信息(如NUP98:Oncogene),评估其在细胞生物学过程中的潜在作用。
- 细胞特异性:分析融合基因在不同细胞类型中的分布模式,确定其表达的细胞特异性。
- 融合类型分析:根据融合断点位置和蛋白质融合类型,预测融合蛋白的结构和功能特性。
- 数据库关联:通过与Mitelman、ChimerKB等数据库的比对,获取已知融合事件的临床和生物学信息。
案例参考
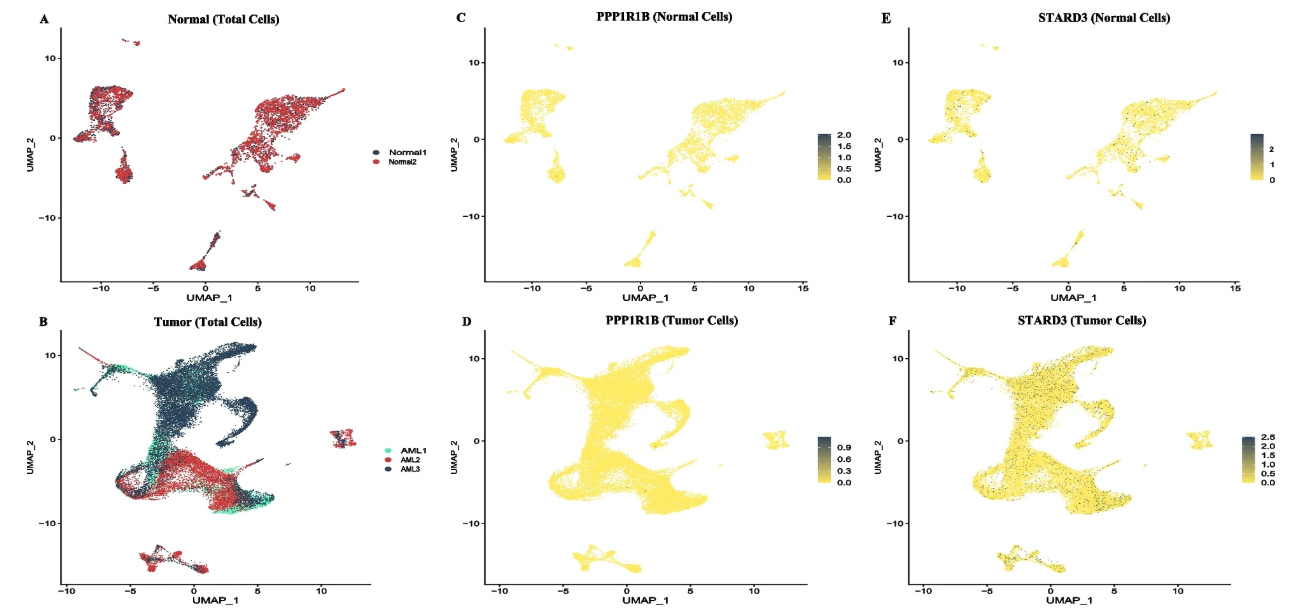
Fusion模块的分析结果可广泛应用于多种研究场景,特别是在白血病研究领域具有重要价值。以PPP1R1B::STARD3融合为例:
- 新型融合基因发现:PPP1R1B::STARD3融合是首次在急性髓系白血病(AML)中报道的融合事件,通过单细胞Fusion分析,可以精确定位携带该融合的细胞群体,了解其在肿瘤异质性中的分布模式。
- 治疗靶点发现:该融合基因涉及胆固醇代谢和PI3K/AKT信号通路,STARD3参与细胞内胆固醇运输,PPP1R1B在多种实体瘤中作为癌基因发挥作用,其融合产物可能成为新的治疗靶点。
- 疾病诊断标志物:该融合基因在AML患者中特异性表达,而在B细胞急性淋巴细胞白血病(B-ALL)中未见报道,具有作为AML诊断标志物的潜力。
推荐的实践路径是:
- 融合筛选:利用融合基因表格中的支持reads数、FFPM等指标,筛选高可信度的融合事件。
- 细胞定位:通过UMAP/TSNE可视化,确定融合基因在不同细胞群体中的分布情况。
- 功能注释:结合数据库注释信息,评估融合基因的生物学意义和潜在功能影响。
- 验证实验:对重要的融合事件进行后续实验验证,如RT-PCR、FISH等技术。
注意事项与最佳实践
WARNING
融合基因检测结果中可能存在假阳性,需要结合多个指标进行筛选,如JunctionReadCount、LargeAnchorSupport等。对于重要的融合事件,建议进行实验验证。
- 数据质量控制:确保输入数据质量良好,通过fastp等工具进行质控,过滤低质量reads,提高融合检测的准确性。
- 参数优化:根据具体研究需求,合理调整分析参数,如物种选择、过滤阈值等。
- 结果验证:对检测到的重要融合事件,建议使用RT-PCR、Sanger测序等方法进行实验验证。
- 生物学解读:结合现有文献和数据库信息,对融合事件进行深入的生物学解读,避免过度解读或误读。
常见问题(FAQ)
Q:如何评估融合基因的可信度?
A:主要参考以下指标:高JunctionReadCount和SpanningFragCount、存在LargeAnchorSupport、正常的Left/RightBreakEntropy值(通常在1.5-2.0之间)、具有已知的生物学功能注释等。Q:为什么有些融合事件在UMAP/TSNE图上分布较散?
A:这可能是由于融合事件在多个细胞群体中都有表达,或者样本中存在细胞异质性较高的情况。需要结合具体的生物学背景进行解释。Q:如何区分真正的融合基因和假阳性?
A:除了关注统计指标外,还可以参考以下几点:融合基因是否在多个公共数据库中有记录、断点是否位于内含子区域且符合GT-AG剪接信号、融合产物是否具有潜在的生物学功能等。Q:分析结果中发现了大量线粒体基因相关的融合,这是正常的吗?
A:线粒体基因(MT-开头)参与的融合事件较为常见,但很多可能是技术原因导致的假阳性。建议结合注释信息和生物学知识进行筛选,重点关注与已知疾病相关的融合事件。
参考文献
- Haas, B.J., Dobin, A., Li, B. et al. Accuracy assessment of fusion transcript detection via read-mapping and de novo fusion transcript assembly-based methods. Genome Biol 20, 213 (2019). https://doi.org/10.1186/s13059-019-1842-9
- Haas B , Dobin A , Stransky N ,et al.STAR-Fusion: Fast and Accurate Fusion Transcript Detection from RNA-Seq[J]. 2017.DOI:10.1101/120295.
- Kumar-Sinha C, Tomlins SA, Chinnaiyan AM. The emergence of gene fusions as biomarkers and therapeutic targets. Cancer Discov. 2015;5(1):36-47. doi:10.1158/2159-8290.CD-14-1014
- Detection of novel PPP1R1B::STARD3 fusion transcript in acute myeloid leukemia: a case report. 2023. Case Report. doi:10.1186/s13256-024-04536-w
