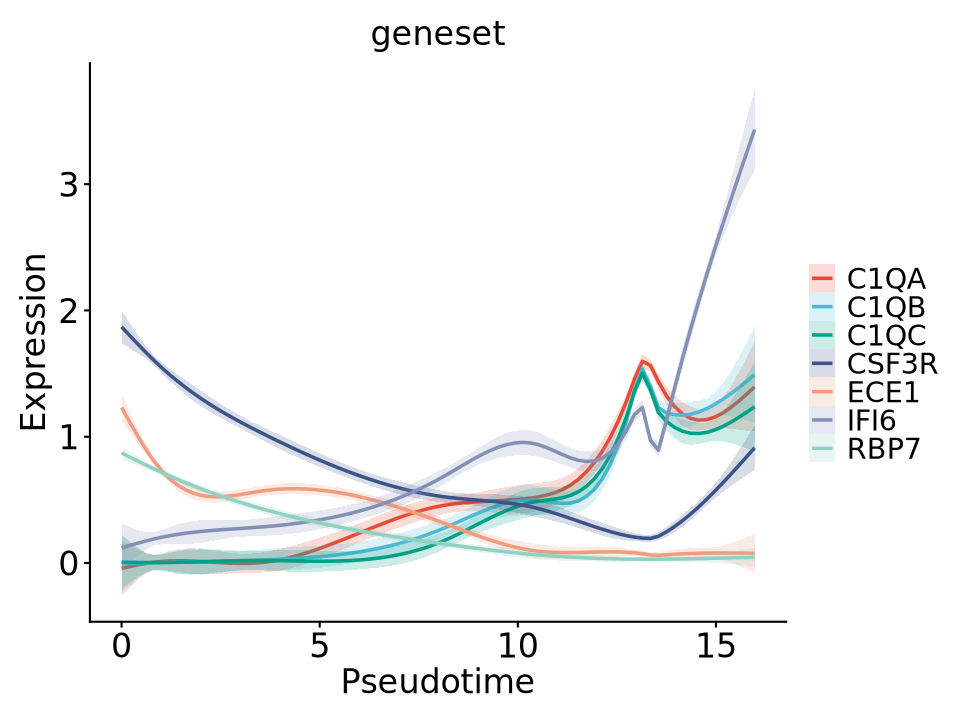
单细胞基因表达动态解析:拟时序基因表达量曲线拟合
时长: 4 分钟
字数: 727 字
更新: 2026-02-27
阅读: 0 次
环境配置
R
# 加载脚本运行依赖的R包
library(monocle)
library(Seurat)
library(dplyr)
library(tidyverse)
library(ggplot2)
library(ggsci)数据读取
R
#读取数据
gbm_cds <- readRDS("data/AY1740561864613/advanced_analysis/58047/output/monocle2/monocle_final.rds") ### monocle2分析结果
rep <- as.data.frame(pData(gbm_cds)) # 读取表型信息
gene_all <- row.names(gbm_cds@assayData$exprs) #获取gbm_cds中全部基因数据预处理
R
gene_ad <- c("RBP7","ECE1","C1QA","C1QC","C1QB","IFI6","CSF3R") #定义图中要展示的基因,最多展示10个基因R
# gene_ad 与 genes_all 取交集
gene_se <- vector()
for(i in gene_ad){
if(i %in% gene_all){
gene_se <- c(gene_se,i)
}
}R
# 提取基因表达量
for(i in gene_se){
gene_in <- names(pData(gbm_cds))
if (i %in% gene_in){
next
}else{
tmp <- gbm_cds@assayData$exprs[i,] %>% as.data.frame
names(tmp) <- i
tmp <- tmp %>% mutate(barcode=rownames(tmp))
pData(gbm_cds) <- pData(gbm_cds) %>% inner_join(tmp,by="barcode")
rownames(pData(gbm_cds)) <- pData(gbm_cds)$barcode
}
}R
# 合并表达量信息和拟时序信息
data_plot <- pData(gbm_cds) %>% select(Pseudotime,all_of(gene_se)) %>%
pivot_longer(cols = -Pseudotime,names_to = "Gene",values_to = "Expression")拟时序曲线绘制
R
# 设置图形输出尺寸(适用于Jupyter等交互环境)
# repr.plot.height: 图形高度6英寸
# repr.plot.width: 图形宽度8英寸
options(repr.plot.height=6, repr.plot.width=8)
# 创建ggplot对象
ggplot(data = data_plot, mapping = aes(x = Pseudotime,
y = Expression,
color = Gene, # 按基因分组颜色
fill = Gene)) + # 按基因分组填充色
# 使用Nature出版集团配色方案(npg)
ggsci::scale_color_npg(name = "") + # 离散型颜色标尺
ggsci::scale_fill_npg(name = "") + # 离散型填充色标尺
# 添加GAM平滑曲线(置信区间带)
# method: 使用广义加性模型
# formula: 三次平滑样条基函数(cubic spline basis)
# alpha: 置信区间透明度(0-1)
# size: 曲线线宽
geom_smooth(method = "gam",
formula = y ~ s(x, bs = "cs"),
alpha = 0.2,
size = 1) +
# 应用cowplot主题(简洁科研风格)
cowplot::theme_cowplot() +
# 自定义主题细节
theme(
axis.text.x = element_text(size = 20), # X轴刻度标签字号
axis.text.y = element_text(size = 20), # Y轴刻度标签字号
text = element_text(size = 20, family = "ArialMT"), # 全局字体设置
plot.margin = unit(c(1, 1, 1, 1), "char"), # 图形边距(字符单位)
plot.title = element_text(
hjust = 0.5, # 标题居中
size = 20, # 标题字号
family = "ArialMT", # 字体类型
face = "plain" # 无加粗
),
axis.line = element_line(
linetype = 1, # 实线类型
color = "black", # 轴线颜色
linewidth = 0.6 # 轴线宽度
),
axis.ticks = element_line(
linetype = 1, # 刻度线类型
color = "black", # 刻度线颜色
linewidth = 0.6 # 刻度线宽度
)
# legend.position = "none" # 取消图例显示(当前注释状态)
) +
# 坐标轴标签设置
ylab("Expression") + # Y轴标签(基因表达量)
xlab("Pseudotime") + # X轴标签(拟时序分析结果)
ggtitle("geneset") # 主标题
# 保存输出(出版级分辨率)
# filename: 输出文件名
# width: PDF宽度9英寸(约22.86cm)
# height: PDF高度8英寸(约20.32cm)
ggsave("expression.pdf", width = 9, height = 8)